基因在我們的生命中扮演著關鍵角色。生命藍圖™ (Blueprint of Life™) 提供全面的基因檢測,幫助您了解獨特的基因組成、健康風險及潛能。通過252項健康指標,我們的檢測讓您能夠幫助您做出明智的選擇。
通過廣泛的分析,涵蓋

癌症

疾病風險

長壽與
營養

美容與
抗老

遺傳風險
生命藍圖™ 能提供您全面的健康風險資訊。我們的非侵入性基因檢測確保舒適的體驗,準確性不打折扣。
檢測完成後,您會收到詳細且容易理解的報告,並提供諮詢,幫助您擬定個人化健康策略:
預防
生活方式管理
健康促進
如何進行檢測?

❶ 樣本收集
收集DNA可以透過非侵入性的採檢方法變得舒適和簡便,像是從漱口中獲得的口腔細胞。這種方法提供了以下優點:
- 舒適性
口腔細胞收集無痛,不用擔心疼痛的採檢過程。 - 便利性
過程只需用漱口水漱口,然後將漱口水收集到樣本管中。 - 高品質DNA
口腔細胞能夠提供充足且高品質的DNA,適用於後續的基因分析。
❷ 建庫
定序技術發展
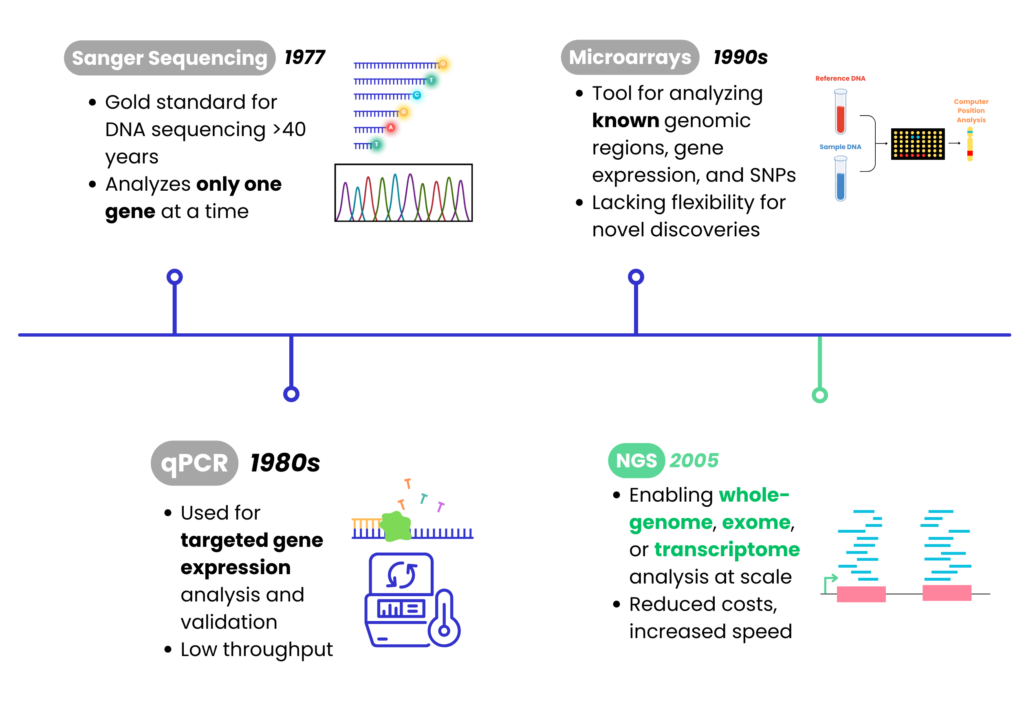
NGS vs. 基因晶片 vs. qPCR 比較
在定序基因數量、基因涵蓋範圍和發現罕見突變等方面,NGS 優於基因晶片 (microarrays) 和 qPCR,使其成為多基因檢測的首選。
| 參數 | 次世代定序 (NGS, Next Generation Sequencing) | 基因晶片 (Microarray) | 定量PCR (qPCR) |
| 偵測原理 | 直接定序,分析DNA序列 | 探針雜交,偵測特定基因變異 | 使用螢光探針,監測PCR擴增的DNA產物 |
| 可偵測變異類型 | 點突變(SNV)、插入/缺失(INDELs)、拷貝數變異(CNV)、結構變異 | 已知的單核苷酸多態性(SNP)或拷貝數變異(CNV) | 已知的單核苷酸多態性(SNP), 插入/缺失(INDELs), 基因表達水平變化 |
| 靈敏度與準確度 | 高,能檢測低頻突變與新發現突變 | 較低,僅偵測預先設計的變異 | 較高,但突變覆蓋範圍有限 |
| 應用範圍 | 非侵入性產前檢測(NIPT)、癌症基因檢測、罕病診斷 | 羊水晶片、族群研究、Biobank | COVID-19診斷、 酒精代謝基因 |
Cell3™ Target: Nexome – 提供超越一般 WES 的基因資訊
Cell3TM Target: Nexome 是一個新一代外顯子定序,突破一般全外顯子測序(WES)的侷限性。
透過先進的探針設計和優越的覆蓋範圍與均勻性,Cell3™ Target: Nexome 提供了一個全面的基因檢測和研究應用解決方案。
檢測面板包括
產前診斷、癲癇和藥物基因組學(PGx)相關的基因

外顯子 (exon-level) 的缺失和重複

位在非編碼區(non-coding region)遺傳疾病相關的變異

與 OMIM 資料庫(4,090 基因)相對應的 RefSeq 中啟動子區域、5′ 和 3′ UTR 序列
大約 85% 由DNA突變所引起的疾病源自於外顯子區域的變異。
Cell3™ Target: Nexome 能夠涵蓋比市面上一般外顯子產品多出 30% 的變異
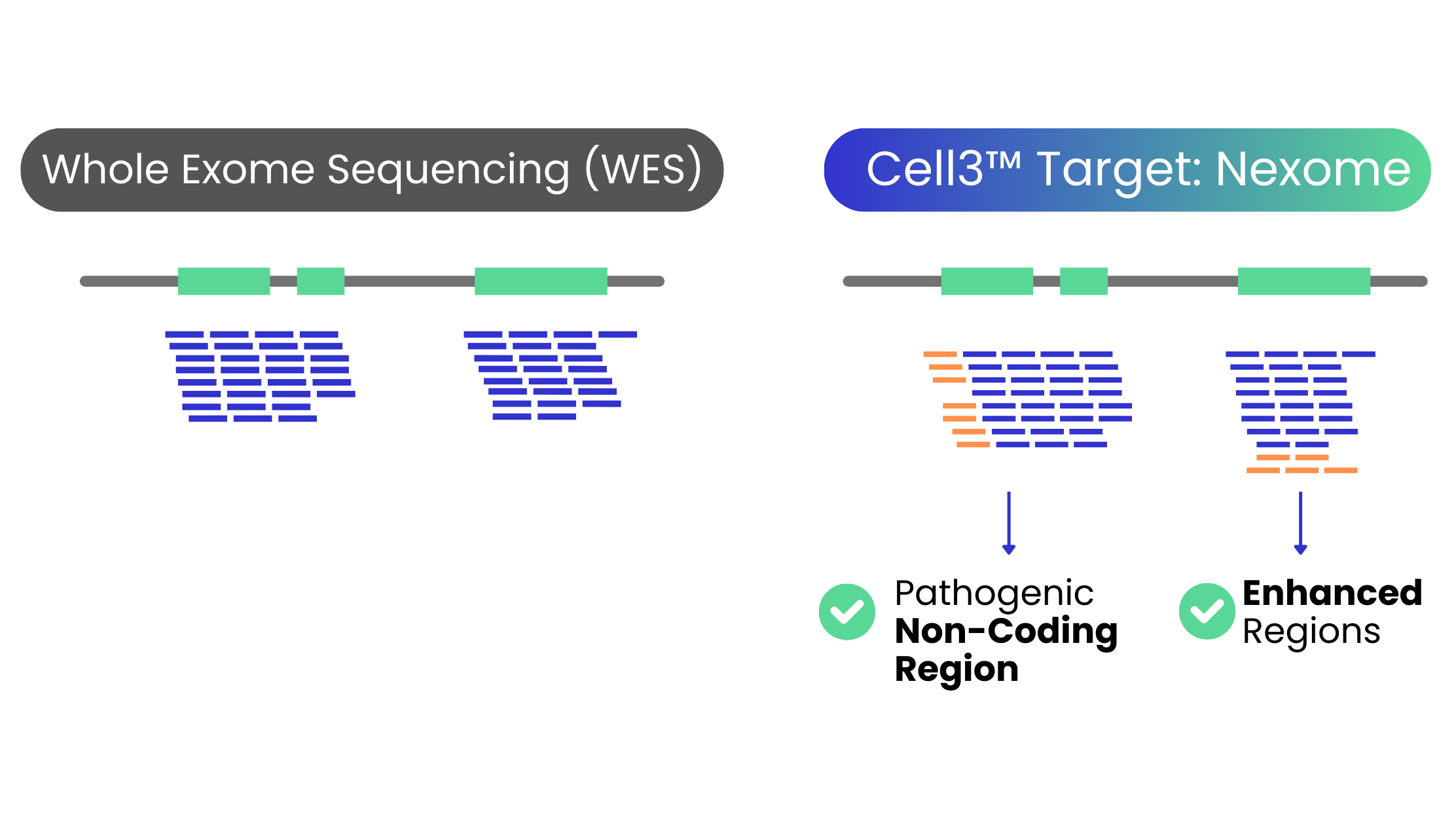
| 特徵 | 傳統 WES | Cell3TM Target: Nexome |
| 基因組覆蓋範圍 | 主要聚焦於蛋白質編碼區域(基因組的 1-2%) | 基因組的蛋白質編碼區域 + 臨床相關的非編碼區域 |
| 偵測的變異類型 | SNVs 和 INDELs,但需要額外測試 CNVs | 單核苷酸變異(SNVs)、插入/缺失(INDELs)和拷貝數變異(CNVs)於一個測試中 |
| 診斷率 | 只限於編碼變異,可能漏掉一些臨床相關變異 | 偵測比標準外顯子面板多達 30% 的變異 |
| 效率與成本 | 需要為 CNVs 進行單獨測試,這會增加成本和複雜性 | 通過將多個測試整合為一個,簡化診斷過程,可能減少整體成本 |
| 應用 | 一般基因診斷,但可能無法提供相同程度的全面分析 | 產前診斷、癲癇評估,以及需要全面基因分析的案例 |
❸ 報告
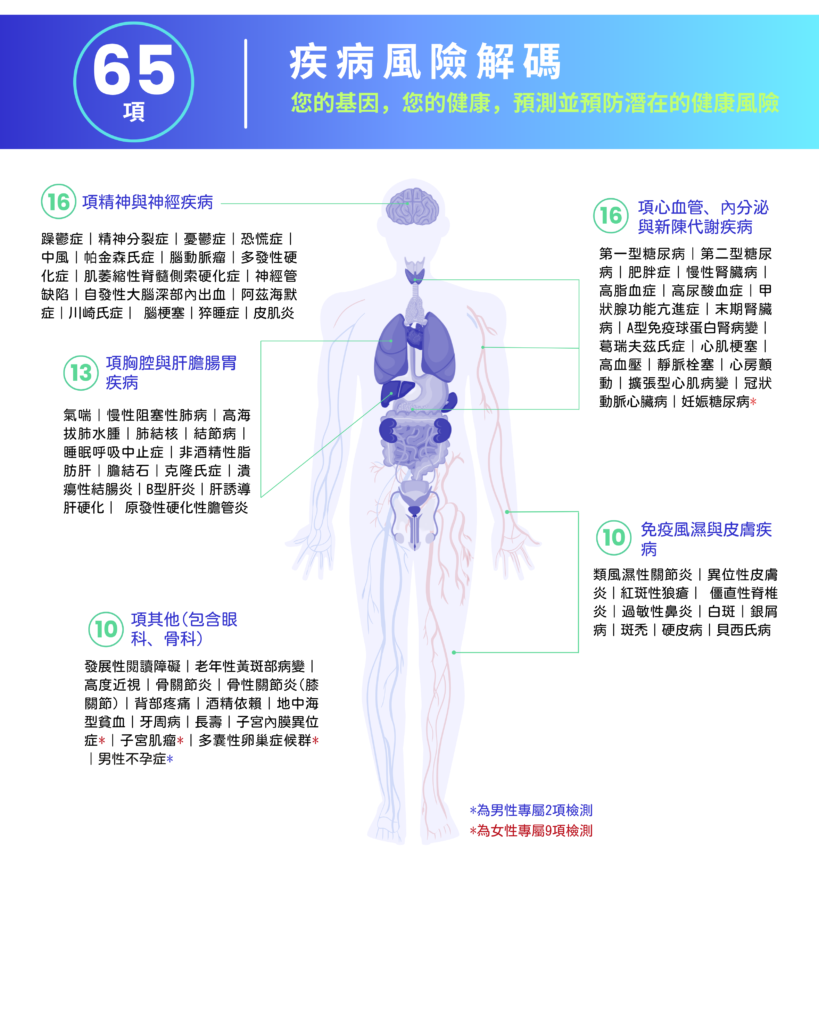
🎯 涵蓋超過 200 項檢測
- 16 項精神與神經疾病
- 13 項胸腔與肝膽腸胃疾病
- 16 項心血管,內分泌與新陳代謝疾病
- 10 項免疫風濕與皮膚疾病
- 10 項其他(包含眼科,骨科)
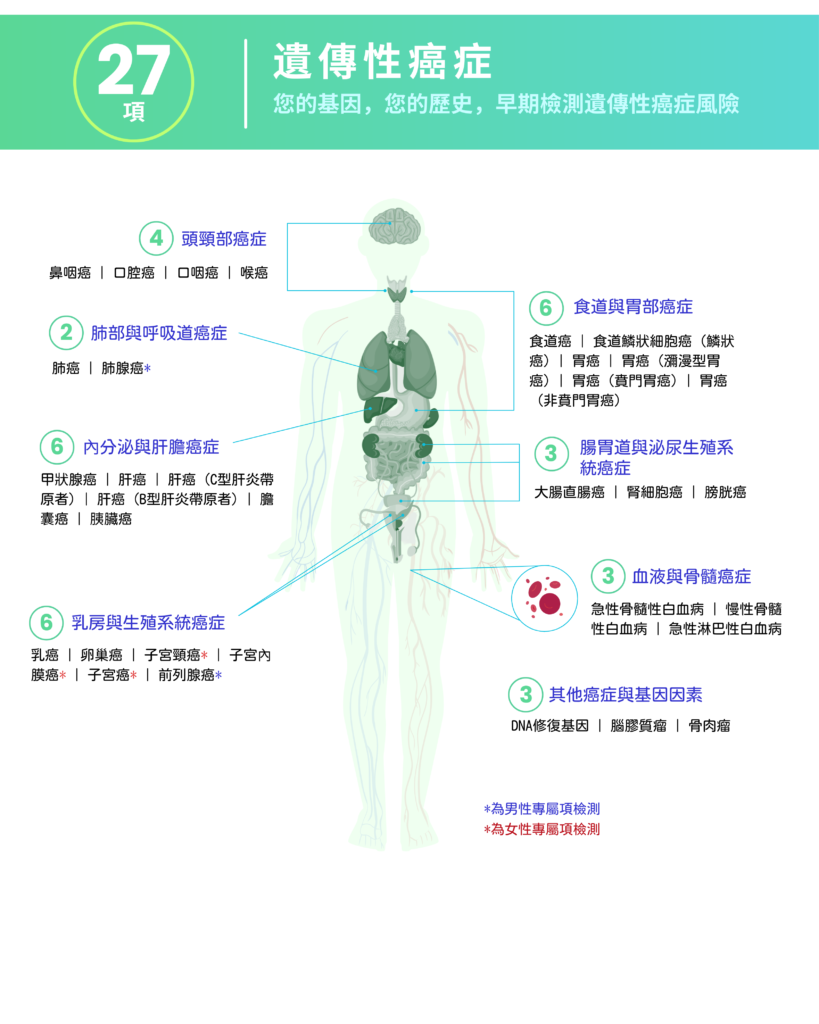
- 4 頭頸部癌症
- 2 肺部與呼吸道癌症
- 6 內分泌與肝膽癌症
- 6 乳房與生殖系統癌症
- 6 食道與胃部癌症
- 3 腸胃道與泌尿生殖系統癌症
- 3 血液與骨髓癌症
- 3 其他癌症與基因因素
- 9 體格與體質
- 7 味覺與嗅覺敏感度
- 4 食飲習慣與營養吸收
- 2 新陳代謝與體重控制
- 14 減重基因
- 13 維生素與礦物質(血液濃度)
- 16 個人特質
- 11 醫學美容
- 14 天分
- 10 其他健康因素
- 6 血液疾病
- 26 內分泌與代謝疾病
- 11 神經與肌肉疾病
- 4 骨骼與結締組織疾病
- 6 甲狀腺疾病
- 7 其他系統遺傳疾病
了解更多 疾病風險解碼基因檢測 項目
符合亞洲人群的基因檢測資料庫
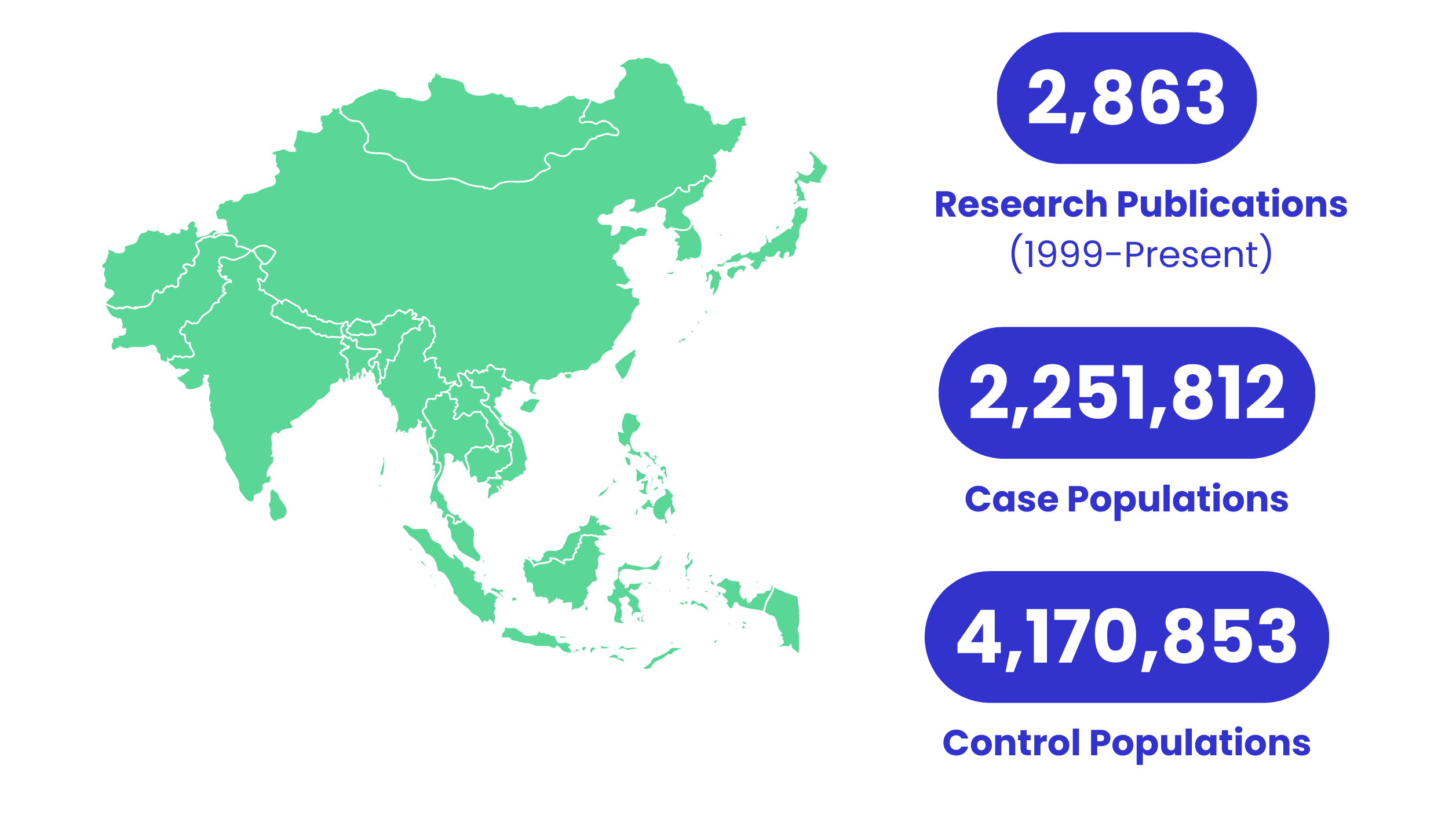
我們的檢測項目經過精心挑選,並與全面的亞洲族群資料庫對照,確保我們的檢測結果能針對亞洲族群獨特的基因型量身定制。這種方法能夠提供準確且高度相關的基因資訊,符合華人的基因特質。
我們從全球資料庫中精選了大量研究文獻,重點關注與亞洲人群相關的研究。這些豐富的資料庫包含了1999年至今的 2,863 篇研究文章,涵蓋了600萬人以上的研究成果幫助您擬定個人化且有效的健康管理方案。
完整的認證實驗室:國際認證
LDTS
ISO 15189
TAF

❹ 檢測後諮詢服務
檢測後諮詢:結果諮詢與專業建議
在收到基因檢測結果後,如果對於報告內容有所疑問,我們的檢測後諮詢能與您討論您的檢測結果,確保能充分理解您的檢測結果及其對您的健康和家庭的影響。
明智的決策
幫助您根據基因檢測結果做出關於健康和家庭的規劃
個人化護理
通過討論潛在的治療選項並轉介專家,促進個人化的健康管理
References
- Nature news. https://www.nature.com/scitable/topicpage/inheritance-of-traits-by-offspring-follows-predictable-6524925/
- Loewe, L. (2008) Genetic mutation. Nature Education 1(1):113
- Stallard, T. (2023) Rare disease care across asia pacific, Sandpiper.
- Hlawulani (2019) New Scientific Paper confirms 300 million people living with a rare disease worldwide, Rare Diseases International.
- Pesheva, E. (2023) Researchers able to determine the effects of genes and environment in 560 common conditions, Harvard Gazette.
- Hanany, M., Rivolta, C., & Sharon, D. (2020). Worldwide carrier frequency and genetic prevalence of autosomal recessive inherited retinal diseases. Proceedings of the National Academy of Sciences, 117(5), 2710–2716.
- Abdul, Q. A., Yu, B. P., Chung, H. Y., Jung, H. A., & Choi, J. S. (2017). Epigenetic modifications of gene expression by lifestyle and environment. Archives of Pharmacal Research, 40(11), 1219–1237. https://doi.org/10.1007/s12272-017-0973-3
- Alegría-Torres, J. A., Baccarelli, A., & Bollati, V. (2011). Epigenetics and Lifestyle. Epigenomics, 3(3), 267–277.
- CDC. (2025, January 31). Epigenetics, Health, and Disease. Genomics and Your Health. https://www.cdc.gov/genomics-and-health/epigenetics/index.html
- Advantages of NGS Over Other Molecular Methods. (2020). Illumina.com. https://sapac.illumina.com/science/technology/next-generation-sequencing/beginners/advantages.html
- UF scientists test mouthwash method of collecting DNA – UF Health. (2023). Ufhealth.org. https://ufhealth.org/news/2002/uf-scientists-test-mouthwash-method-collecting-dna
- Zayats, T., Young, T. L., Mackey, D. A., Malecaze, F., Calvas, P., & Guggenheim, J. A. (2009). Quality of DNA Extracted from Mouthwashes. PLoS ONE, 4(7). https://doi.org/10.1371/journal.pone.0006165
- Lelieveld, S. H., Spielmann, M., Mundlos, S., Veltman, J. A., & Gilissen, C. (2015). Comparison of Exome and Genome Sequencing Technologies for the Complete Capture of Protein-Coding Regions. Human Mutation, 36(8), 815–822.
- Zhao, Y., Fang, L. T., Shen, T., Choudhari, S., Talsania, K., Chen, X., Shetty, J., Kriga, Y., Tran, B., Zhu, B., Chen, Z., Chen, W., Wang, C., Jaeger, E., Meerzaman, D., Lu, C., Idler, K., Ren, L., Zheng, Y., & Shi, L. (2021). Whole genome and exome sequencing reference datasets from a multi-center and cross-platform benchmark study. Scientific Data, 8(1). https://doi.org/10.1038/s41597-021-01077-5
- Barbitoff, Y. A., Polev, D. E., Glotov, A. S., Serebryakova, E. A., Shcherbakova, I. V., Kiselev, A. M., Kostareva, A. A., Glotov, O. S., & Predeus, A. V. (2020). Systematic dissection of biases in whole-exome and whole-genome sequencing reveals major determinants of coding sequence coverage. Scientific Reports, 10(1). https://doi.org/10.1038/s41598-020-59026-y